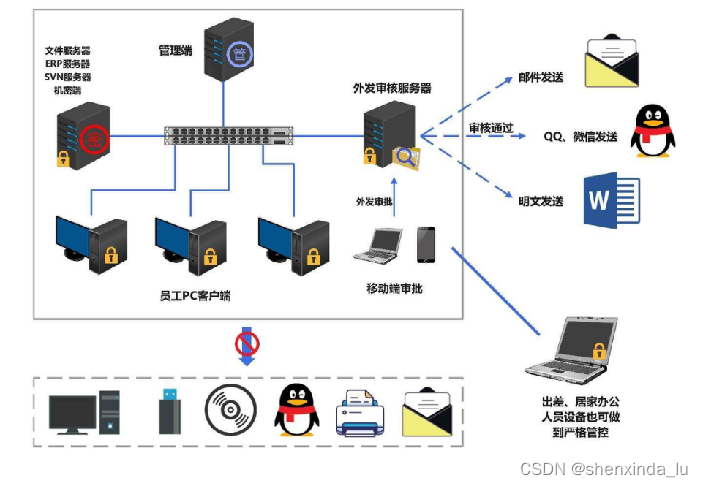
STRING数据库简介
- STRING是一个包含已知和预测蛋白质-蛋白质相互作用的数据库。
- 数据库涵盖了直接(物理)和间接(功能)相互作用。
- 包含来自实验仓库、计算预测方法和公共文本集合的多种证据来源。
- 覆盖超过2400万个蛋白质,涉及5090个生物体。
- 提供R包STRINGdb以方便用户从R访问数据库。
初始化STRINGdb对象
- 使用
STRINGdb$new()函数实例化STRINGdb参考类。 - 可以指定STRING版本、分数阈值、网络类型和输入目录。
- 分数阈值默认为400,低于此阈值的交互不会加载到对象中。
- 网络类型可选“full”(全功能网络)或“physical”(物理子网络)。
STRINGdb的方法和帮助
STRINGdb$methods()列出所有可用方法。STRINGdb$help(get_graph")显示特定方法的文档。
获取网络图形
get_graph()返回整个STRING网络的igraph对象。- 建议使用iGraph包的功能进行网络搜索和分析。
聚类分析
- 使用iGraph包的聚类算法
-
STRINGdb 包含了由 iGraph 提供的多种聚类或社区检测算法,包括:
1. fastgreedy
2. walktrap
3. spinglass
-